ㅤㅤ
ㅤㅤ
32. During DNA replication of an eukaryotic cell, a guanine (G) is mistakenly paired with a thymine (T) and escapes the initial proofreading by DNA polymerase. This G-T pair becomes fully incorporated into the double helix. Which of the following best describes how the cell corrects this mismatch/error?
ㅤㅤ
ㅤㅤ
<32. 在真核細胞進行DNA複製期間,一個鳥嘌呤(G)錯誤地與一個胸腺嘧啶(T)配對,並逃過了DNA聚合酶最初的校對機制。這個G-T鹼基對完全併入雙螺旋結構中。以下哪一項最能描述細胞如何修正這個錯配/錯誤?>
ㅤㅤ
ㅤㅤ
ㅤㅤ
ㅤㅤ
(A)
ㅤㅤ
The cell utilizes DNA photolyase to break the hydrogen bonds between the mismatched bases and flip them into the correct orientation.
ㅤㅤ
<細胞利用DNA光解酶來斷裂錯配鹼基之間的氫鍵,並將它們翻轉至正確的方位。>
ㅤㅤ
題目說:
"斷開錯配鹼基的氫鍵(G–T、A–C)並翻轉修正"
ㅤㅤ
這其實是在描述 錯配修復(Mismatch repair, MMR),而不是 photolyase。
ㅤㅤ
ㅤㅤ
ㅤㅤ
ㅤㅤ
photolyase 不負責這種情況
photolyase 的功能是:修復紫外線造成的 thymine dimer(T–T 之間的共價鍵連結)
ㅤㅤ
ㅤㅤ
ㅤㅤ
ㅤㅤ
所以差別是:
ㅤㅤ
G–T、A–C 錯配 → MMR(切除錯誤片段再重複合成)
ㅤㅤ
T–T dimer → photolyase(用光能直接修復 UV 損傷))
ㅤㅤ
(B)
ㅤㅤ
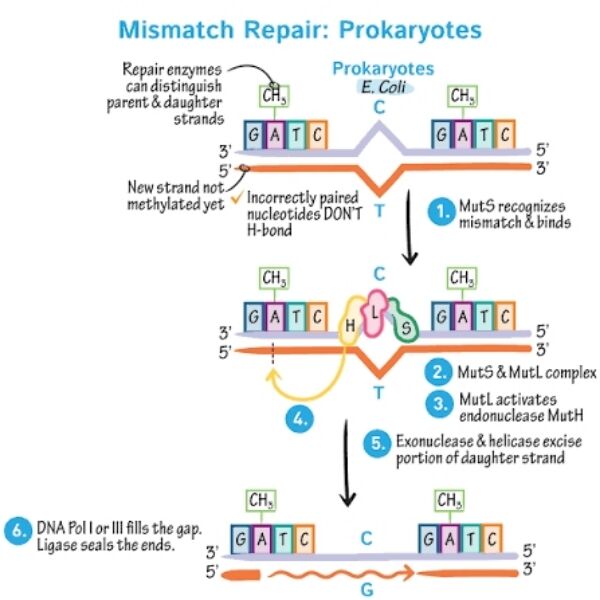
The cell utilizes specific endonucleases to recognize the helical distortion and identify the newly synthesized strand to cut out the segment containing the incorrect nucleotide.
ㅤㅤ
ㅤㅤ
<細胞利用特定的內切核酸酶來辨識螺旋結構的扭曲,並識別新合成的股,以切除含有錯誤核苷酸的片段。>對,
(B) Endonuclease in MMR 這才是正確的機制。Mismatch repair 會偵測 DNA 螺旋的扭曲,辨認新合成的股,然後用內切核酸酶切掉錯誤片段,再由 DNA polymerase 補上正確序列。
ㅤㅤ
(C)
英文:
The cell utilizes RNA primase to recognize the mismatched sites, where it initiates reverse transcription to replace the DNA segment with a temporary RNA patch.
ㅤㅤ
中文:
細胞利用RNA引子酶來辨識錯配位點,並在此啟動反轉錄,以用暫時的RNA補片替換DNA片段。
C) 錯
RNA primase + reverse transcription + RNA patch
有三個錯
① RNA primase 根本不是修DNA錯誤用的
DNA primase
它會
在 DNA 複製時「做RNA primer」
❌ 不負責辨識錯配 , 不負責修復DNA
ㅤㅤ
ㅤㅤ
② 沒有reverse transcription修DNA這件事
反轉錄是:
RNA → DNA(例如病毒或實驗室)把RNA反轉錄成DNA
DNA 修復<DNA → DNA(修補)>
應該用的是:
DNA polymerase
endonuclease
ligase
ㅤㅤ
③ DNA修復不會用 RNA patch 替換錯誤DNA,真正修復是:
切掉DNA → DNA polymerase補回
不是用RNA暫時補洞
ㅤㅤ
RNA primase + reverse transcription =>完全不相關,這是捏造的機制
ㅤㅤ
(D)
英文:
The cell utilizes DNA ligase to identify the incorrect hydrogen bonding site and uses its 5' to 3' exonuclease activity to chew back the faulty nucleotide.
ㅤㅤ
中文:
細胞利用DNA連接酶來辨識錯誤的氫鍵結合位點,並利用其5'至3'的外切核酸酶活性,將錯誤的核苷酸切除回去。
錯
1,DNA ligase(DNA連接酶)
真正功能是把DNA片段黏回去,不是用來辨識錯誤
2.5'→3' exonuclease 用錯酵素
這個活性通常是DNA polymerase I(細菌)才有
,功能是移除RNA primer或前方DNA片段,不是用來辨識錯配氫鍵
3.真正錯配修復錯配是:Mismatch Repair (MMR)
ㅤㅤ
(E)
英文:
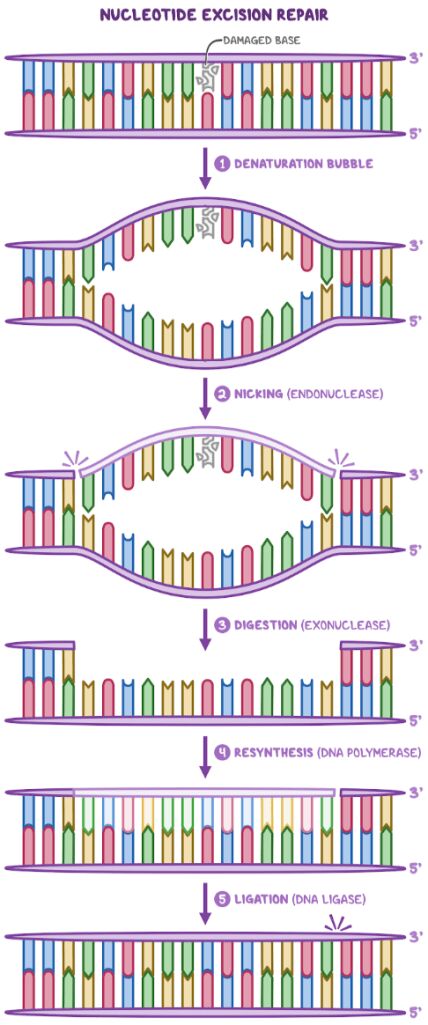
The cell utilizes a multi-protein complex to scan the DNA for bulky lesions and remove a 12-30 nucleotide oligomer of the damaged strand.
ㅤㅤ
中文:
細胞利用一個多蛋白複合體來掃描DNA上的大體積損傷,並移除損傷股上12-30個核苷酸長的寡聚體。
ㅤㅤ
ㅤㅤ
Mismatch Repair(MMR)
當 DNA 複製時發生鹼基配對錯誤(例如 G–T 或 A–C),但 DNA 雙股結構仍然維持正常的雙螺旋形態,沒有明顯變形。
細胞會啟動 Mismatch Repair (MMR) 系統來修正,先辨識錯配位置,再切除包含錯誤鹼基的新生 DNA 片段,接著由 DNA polymerase 重新合成正確序列,最後由 ligase 封口完成修復。
ㅤㅤ
Nucleotide Excision Repair(NER)
當 DNA 遭受紫外線或化學物質傷害時(例如 thymine dimer 或 bulky lesion),會造成 DNA 雙螺旋結構明顯扭曲或變形,影響正常配對,屬於「不是單一字錯,而是整段結構被壓壞」。
細胞會啟動 Nucleotide Excision Repair (NER) 系統,由多蛋白複合體掃描 DNA,辨識結構異常,並切除約 12–30 個核苷酸的受損片段,之後再由 DNA polymerase 補回正確序列,最後由 ligase 完成連接。
ㅤㅤ
ㅤㅤ
ㅤㅤ
-